لوئیجی ریکاردی 1 ، رزا مازئو 2,*©، آنجلو راffaele Marcotrigiano 1 , گوگلیلمو راینالدی 3 ، پائولو آیووینو 4 ویتو زونو 1 ، استفانو پاوان 1© و کونستا لوتی 2,*
- 1 گروه خاک، علوم گیاهی و غذایی، ژنتیک گیاهی و واحد اصلاحی دانشگاه باری، Via Amendola 165/A، 70125 Bari، Italy; luigi.ricciardi@uniba.it (LR)؛angelo.marcotrigiano@uniba.it (ARM)؛ vito.zonno@uniba.it (VZ)؛ stefano.pavan@uniba.it (SP)
- 2 گروه علوم کشاورزی، غذا و محیط زیست، دانشگاه فوجیا، Via Napoli 25، 71122 Foggia، ایتالیا
- 3 گروه علوم زیستی، بیوتکنولوژی و داروسازی زیستی، دانشگاه باری، Via Orabona 4، 70125 Bari، Italy; guglielmo.rainaldi@uniba.it
- 4 بخش فناوریهای انرژی، بخش انرژی زیستی، پالایشگاه زیستی و شیمی سبز، مرکز تحقیقات ENEA Trisaia، SS 106 Ionica، کیلومتر 419+500، 75026 Rotondella (MT)، ایتالیا؛ paolo.iovieno@enea.it
* نامه rosa.mazzeo@unifg.it (RM)؛ concetta.lotti@unifg.it (CL)
چکیده:
پیاز (Allium cepa L.) دومین محصول سبزی مهم در سراسر جهان است و به دلیل مزایای سلامتی آن به طور گسترده مورد استقبال قرار می گیرد. با وجود اهمیت اقتصادی قابل توجه و ارزش آن به عنوان غذای کاربردی، پیاز با توجه به تنوع ژنتیکی آن مورد بررسی قرار نگرفته است. در اینجا، ما تنوع ژنتیکی "پیاز قرمز Acquaviva" (ARO) را بررسی کردیم، یک نژاد بومی با سابقه کشت صد ساله در یک شهر کوچک در استان باری (آپولیا، جنوب ایتالیا). مجموعه ای از 11 نشانگر ریزماهواره برای بررسی تنوع ژنتیکی در مجموعه ژرم پلاسم متشکل از 13 جمعیت ARO و سه نوع تجاری رایج استفاده شد. تجزیه و تحلیل ساختار ژنتیکی با روشهای پارامتریک و ناپارامتریک نشان داد که ARO یک مخزن ژنی کاملاً تعریف شده را نشان میدهد، که به وضوح از تودههای Tropea و Montoro که اغلب با آن اشتباه گرفته میشود، متمایز است. به منظور ارائه توصیفی از پیازهایی که معمولاً برای مصرف تازه استفاده میشوند، محتوای جامد محلول و تندی مورد ارزیابی قرار گرفت که شیرینی بالاتری را در ARO نسبت به دو نژاد بومی ذکر شده در بالا نشان داد. به طور کلی، مطالعه حاضر برای ارزش گذاری آتی ARO مفید است، که می تواند از طریق برچسب های کیفیتی که می تواند به محدود کردن تقلب های تجاری و بهبود درآمد خرده مالکان کمک کند، ترویج شود.
معرفی
جنس آلیوم شامل حدود 750 گونه [1] است که در این میان پیاز (Allium cepa L., 2n = 2x = 16) یکی از گستردهترین گونهها است. A. cepa دارای یک چرخه دوسالانه و رفتار تولیدمثلی است. امروزه تولید جهانی پیاز (97.9 میلیون تن) آن را به دومین محصول مهم سبزیجات پس از گوجه فرنگی تبدیل کرده است [2]. از زمان های قدیم، پیاز پیاز هم به عنوان غذا و هم در کاربردهای دارویی عامیانه استفاده می شده است. در واقع، مصریان باستان چندین فرمول درمانی را بر اساس استفاده از سیر و پیاز در پاپیروس پزشکی 1550 قبل از میلاد، Codex Ebers [3] گزارش کردهاند.
این سبزی همه کاره و سالم به صورت خام، تازه یا به عنوان محصول فرآوری شده مصرف می شود و برای بهبود طعم بسیاری از غذاها استفاده می شود. چندین مطالعه اخیر ادعا میکنند که مصرف پیاز ممکن است خطر بیماریهای قلبی عروقی [4,5،6]، چاقی [7]، دیابت [8] و انواع مختلف سرطان را کاهش دهد [10-XNUMX]. خواص پیاز برای سلامتی اغلب به سطوح بالای دو دسته از ترکیبات تغذیهای نسبت داده میشود: فلاونوئیدها و آلک(ان)یل سیستئین سولفوکسیدها (ACSOs). دسته اول شامل فلاونول ها و آنتوسیانین ها می شود. کوئرستین فلاونول اصلی قابل تشخیص است که به دلیل خواص آنتی اکسیدانی قوی و ضد التهابی در مهار رادیکال های آزاد و اتصال یون های فلزات واسطه شناخته شده است. [11]; در حالی که آنتوسیانین ها به برخی از انواع پیاز رنگ قرمز/بنفش می دهند. در مورد ACSO ها، فراوان ترین آنها ایزوآلیین [(+)-trans-S-1-propenyl-L-cysteine sulfoxide] است. [12]اسید آمینه گوگردی غیر فرار و غیر پروتئین زا ذخیره شده در سلول ها است که به طور غیر مستقیم مسئول عطر و طعم تند پیاز است. [13]. به محض از هم گسیختگی بافت، ایزوآلیین توسط آنزیم آلیناز جدا می شود تا مجموعه ای از ترکیبات فرار (پیروات، آمونیاک، تیوسولفونات ها و پروپانتیال S-oxide) تولید شود که باعث پارگی و ایجاد بوی نامطبوع (تندی) می شود. [14]. تندی پیاز اغلب به عنوان مقدار، در هر گرم وزن تازه، اسید پیروویک تولید شده توسط هیدرولیز اندازه گیری می شود. [1516].
در کشورهای حوزه مدیترانه، به عنوان یکی از مراکز تنوع ثانویه پیشنهاد شده است A. cepa [1718]لامپ های پیاز تنوع زیادی در شکل، اندازه، رنگ، ماده خشک و تندی دارند [19-یک]. علاوه بر این، کوددهی مبتنی بر گوگرد، شیوههای زراعی، نوع خاک، شرایط آب و هوایی و ژنوتیپ ارقام یا نژادهای بومی میتوانند با اعطای ارزشهای ارگانولپتیکی و غذایی خاص بر کیفیت پیاز تأثیر بگذارند. [23-یک]. در ایتالیا، علیرغم در دسترس بودن گسترده ژرم پلاسم پیاز، تنها تعداد کمی از انواع پیاز اغلب تحت مطالعات علمی قرار می گیرند و به درستی مشخص می شوند. [2829].
شناسایی کامل ژنتیکی و فنوتیپی تنوع زیستی کشاورزی برای تضمین حفاظت مناسب از منابع ژنتیکی گیاهی و ترویج استفاده از ژنوتیپهای خاص در زنجیره ارزش بسیار مهم است. [30-یک]. نشانگرهای تکرار توالی ساده (SSR) اغلب برای نقشه برداری انتخاب شده اند [33-یک]، انگشت نگاری DNA و تمایز رقم [36-یک]و برآورد قابل اعتماد تنوع ژنتیکی در داخل و بین نژادهای بومی [39-یک]از آنجایی که آنها مکان خاص، چند آللی هستند، به طور همزمان به ارث می رسند، بسیار قابل تکرار هستند و برای ژنوتیپ خودکار مناسب هستند.
در مطالعه حاضر، ما توجه خود را بر روی یک نژاد بومی سنتی آپولیایی، "پیاز قرمز آکواویوا" (ARO) متمرکز کردیم که طبق روشهای کشاورزی ارگانیک در منطقه کوچکی از شهر Acquaviva delle Fonti در استان باری کشت میشود. (آپولیا، جنوب ایتالیا). پیازهای این نژاد بومی بزرگ و مسطح و قرمز رنگ است و بیشتر در دستور پخت های محلی استفاده می شود. اگرچه ARO نشان کیفیت "Slow Food Presidium" را به دست آورد، تولید آن می تواند بیشتر توسط علائم کیفیت اتحادیه اروپا مانند نشان های جغرافیایی محافظت شده (PGI) و نام مبدا محافظت شده (POD) ترویج و محافظت شود، زیرا ممکن است به محدود کردن کلاهبرداری های تجاری و بهبود درآمد خرده مالکان. در اینجا، نشانگرهای مولکولی SSR به عنوان ابزار قدرتمندی برای ارزیابی تنوع ژنتیکی در بین جمعیتهای ARO و تمایز این نژاد بومی از دو نژاد دیگر پیاز قرمز جنوب ایتالیا استفاده شد. علاوه بر این، ما تندی و محتوای جامد محلول را به منظور ارزیابی طعم ARO در رابطه با تقاضای بازار تخمین زدیم.
نتایج
ایجاد مجموعه ژرم پلاسم پیاز قرمز Acquaviva و خصوصیات مورفولوژیکی
بذرهای 13 جمعیت از نژاد بومی ARO، اهدایی کشاورزان در چارچوب پروژه BiodiverSO Apulia Region برای ایجاد مجموعه ژرم پلاسم ARO استفاده شد.
توصیفکنندههای مورفولوژیکی مربوط به پیاز، پوست و گوشت بر روی ژرم پلاسم ARO و بر روی سه توده پیاز جمعآوری شد که دو توده به نژاد پیاز قرمز تروپیا (TRO) و یکی از نژاد پیاز مسی مونتورو (MCO) تعلق داشتند. 1). تمام لامپ های ARO مسطح بودند و با پوست و گوشت خارجی قرمز با سایه های مختلف قرمز مشخص می شدند. در مقابل، گوشت لامپ های TRO کاملا قرمز بود، در حالی که گوشت لامپ های MCO رنگدانه ضعیفی داشت (جدول S1). تجزیه و تحلیل بیوشیمیایی اجازه می دهد تا محتوای محلول جامد و تندی را ارزیابی کند. همانطور که در جدول گزارش شده است 1, میانگین مقادیر محلول جامد لامپ ها در جمعیت های ARO 7.60 بود و از 6.00 (ARO12) تا 9.50 درجه بریکس (ARO11 و ARO13) متغیر بود. این مقدار بالاتر از مقدار تخمین زده شده برای نژادهای بومی TRO و MCO بود (به ترتیب 4.25 و 6.00 درجه بریکس).

جدول 1. محتوای محلول جامد و ارزشهای تندی در جمعیتهای «پیاز قرمز آکواویوا» (ARO)، «پیاز قرمز تروپیا» (TRO) و «پیاز مس مونتورو» (MCO) ارزیابی شده است *.
| CODE | محتوای جامد محلول (بریکس) | تندی (pقالب-1 FW) | ||
| منظور داشتن | CV y (٪) | منظور داشتن | CV y (٪) | |
| ARO1 | 6.25 D * | 5.65 | 5.84 ab * | 23.78 |
| ARO2 | 7.25 DC | 4.87 | 6.51 | 22.98 |
| ARO3 | 7.50 BCD | 9.42 | 5.28 آب | 22.88 |
| ARO4 | 7.50 BCD | 0.00 | 6.97 | 3.74 |
| ARO 5 | 7.50 BCD | 0.00 | 6.80 | 9.68 |
| ARO6 | 6.25 D | 5.65 | 4.51 آب | 39.18 |
| ARO7 | 7.25 DC | 4.87 | 5.25 آب | 15.44 |
| ARO8 | 9.00 AB | 0.00 | 7.04 | 3.49 |
| ARO9 | 8.25 ABC | 4.28 | 6.84 | 0.15 |
| ARO10 | 7.00 DC | 0.00 | 5.94 آب | 6.57 |
| ARO11 | 9.50 | 7.44 | 5.54 آب | 16.43 |
| ARO12 | 6.00 D | 0.00 | 4.91 آب | 9.70 |
| ARO13 | 9.50 | 7.44 | 6.63 | 24.93 |
| MCO | 6.00 D | 0.00 | 4.18 آب | 2.66 |
| TRO1 | 4.25 E | 8.31 | 2.80 ب | 2.10 |
| TRO2 | 4.25 E | 8.31 | 4.28 آب | 4.79 |
* میانگین هایی با حروف یکسان در حروف بزرگ یا کوچک از نظر آماری در 0.01P یا 0.05P تفاوتی ندارند (تست SNK). y ضریب تغییر.
میانگین مقدار تندی ARO، با استفاده از محتوای اسید پیروویک، 6.00 بود که از 4.51 pmolg متغیر بود.-1 FW (ARO6) تا 7.04 (ARO8). این مقدار بالاتر از مقدار تخمین زده شده در توده های TRO و MCO (3.54 pmolg) بود-1 FW و 4.18 pmol g-1 FW، به ترتیب).
پلی مورفیسم SSR و روابط ژنتیکی بین الحاقات
در مطالعه حاضر، 11 مورد از 37 ترکیب پرایمر SSR آزمایش شده، پلیمورفیسمهای تک جایگاهی را ارائه کردند، یعنی حداکثر دو محصول تقویتی را در یک فرد واحد تولید کردند. به طور کلی، 55 آلل در 320 فرد با تعداد آلل در هر مکان از 2 (ACM147 و ACM 504) تا 11 (ACM132) و مقدار میانگین 5 آلل شناسایی شد (جدول). 2). در جمعیت های فردی، تعداد آلل ها (Na) از 1.94 (ACM147 و ACM504) تا 5.38 (ACM132) متغیر بود، در حالی که تعداد آلل های مؤثر (Ne) از 1.41 (ACM152) تا 2.82 (ACM449) متغیر بود. مغایرت ها بین مقادیر Na و Ne به دلیل وجود آلل هایی با فراوانی کم در جمعیت ها و غلبه تنها چند آلل بود. بالاترین مقدار هتروزیگوسیتی مشاهده شده (Ho) برای ACM138 و ACM449 (0.62) برجسته شد، در حالی که کمترین مقدار مربوط به ACM152 (0.25) بود. هتروزیگوسیتی مورد انتظار (He)، که با انتظارات نظری در جمعیت پانمیتیک مطابقت دارد، از 0.37 (ACM504) تا 0.61 (ACM132، ACM138، و ACM449) متغیر بود. شاخص تثبیت رایت (Fis)، مقادیر نزدیک به صفر (متوسط 0.05) را برای همه نشانگرها نشان می دهد، که مقادیر مشابهی را بین سطوح هتروزیگوسیتی مشاهده شده و مورد انتظار نشان می دهد، همانطور که برای گونه های متقاطع انتظار می رود. کارایی نشانگر SSR فردی در انگشت نگاری ژنتیکی با شاخص محتوای اطلاعات چندشکلی (PIC) با مقدار متوسط 0.48 برآورد شد و از 0.33 (ACM504) تا 0.67 (ACM132) متغیر بود. شاخص کارایی دیگر، شاخص اطلاعات شانون (I) مقدار متوسط 0.84 را نشان می دهد و مقادیر فرض شده از 0.45 (ACM152) تا 1.20 (ACM132) را نشان می دهد.
جدول 2. ویژگی های چندشکلی 11 نشانگر SSR که برای تخمین تنوع ژنتیکی در جمعیت های ARO، TRO و MCO استفاده می شود. تعداد کل آلل ها (Na)، محدوده اندازه باند، و شاخص محتوای اطلاعاتی چند شکلی (PIC) به مجموعه کل 320 فرد ژنوتیپ شده در این مطالعه مراجعه کنید. تعداد آلل (Na)، تعداد آلل مؤثر (Ne)، هتروزیگوسیتی مشاهده شده (Ho)، هتروزیگوسیتی مورد انتظار (He)، شاخص تثبیت (F)is، و شاخص اطلاعات شانون (I) به میانگین مقادیر محاسبه شده از 16 جمعیت، که هر کدام توسط 20 فرد تشکیل شده است، اشاره دارد.
| مکان. | کل Na | محدوده اندازه (bp) | PIC | منظور داشتن | |||||
| Na | Ne | Ho | He | I | Fis | ||||
| ACM91 | 4 | 189-205 | 0.40 | 2.63 | 1.72 | 0.38 | 0.39 | 0.66 | 0.04 |
| ACM101 | 4 | 229-241 | 0.52 | 2.94 | 2.37 | 0.53 | 0.56 | 0.92 | 0.06 |
| ACM132 | 11 | 186-248 | 0.67 | 5.38 | 2.78 | 0.55 | 0.61 | 1.20 | 0.09 |
| ACM138 | 5 | 242-272 | 0.66 | 3.69 | 2.82 | 0.62 | 0.61 | 1.09 | -0.02 |
| ACM147 | 2 | 264-266 | 0.37 | 1.94 | 1.83 | 0.44 | 0.44 | 0.62 | -0.01 |
| ACM152 | 4 | 228-244 | 0.25 | 2.38 | 1.41 | 0.25 | 0.27 | 0.45 | 0.07 |
| ACM235 | 4 | 286-298 | 0.41 | 2.81 | 1.77 | 0.44 | 0.41 | 0.72 | -0.06 |
| ACM446 | 6 | 108-120 | 0.56 | 3.50 | 2.48 | 0.49 | 0.58 | 1.01 | 0.16 |
| ACM449 | 8 | 120-140 | 0.66 | 4.88 | 2.82 | 0.62 | 0.61 | 1.18 | -0.03 |
| ACM463 | 5 | 202-210 | 0.47 | 3.38 | 1.95 | 0.46 | 0.48 | 0.83 | 0.05 |
| ACM504 | 2 | 188-192 | 0.33 | 1.94 | 1.64 | 0.30 | 0.37 | 0.54 | 0.20 |
| منظور داشتن | 5 | 0.48 | 3.22 | 2.15 | 0.46 | 0.48 | 0.84 | 0.05 |
در میان جمعیت ها، ARO3، ARO6، ARO8، ARO10، TRO1 و MCO سطح بالایی از تنوع ژنتیکی را نشان دادند (Ho > 0.5)، در حالی که کمترین تنوع در جمعیت ARO7 (Ho = 0.27) مشاهده شد (جدول تکمیلی S2). به طور کلی، تمام الحاق ها F را نشان می دهندis مقادیر نزدیک به صفر (Fis مقدار متوسط = 0.054)، همانطور که در شرایط جفت گیری تصادفی انتظار می رود.
تجزیه و تحلیل واریانس مولکولی و ساختار ژنتیکی
تقسیم بندی سلسله مراتبی تنوع ژنتیکی بین و درون جمعیت ها توسط AMOVA محاسبه شد. نتایج بخش قابل توجهی از تنوع ژنتیکی در جمعیت ها (87٪) را برجسته کرد. تنوع بین جمعیت ها، 13 درصد، بسیار معنی دار بود (P < 0.001) (جدول 3). مقادیر جفتی پارامتر Fpt، مشابه شاخص تثبیت Fst رایت، از 0.002/2 (ARO10/ARO0.468) تا 7/2 (AROXNUMX/TROXNUMX)، معنی دار بود (P < 0.05)، به جز نه مقایسه زوجی (جدول تکمیلی S3).
جدول 3. تجزیه و تحلیل واریانس مولکولی 320 ژنوتیپ از 16 جمعیت آلیوم سیپا L.
| منبع | df | مجموع مربعات | تخمین واریانس | واریانس (%) | Fpt | P |
| در میان جمعیت ها | 15 | 458.63 | 1.16 | ٪۱۰۰ | ||
| درون جمعیت ها | 304 | 2272.99 | 7.50 | ٪۱۰۰ | 0.134 | 0.001 |
| جمع | 319 | 2731.62 | 8.66 |
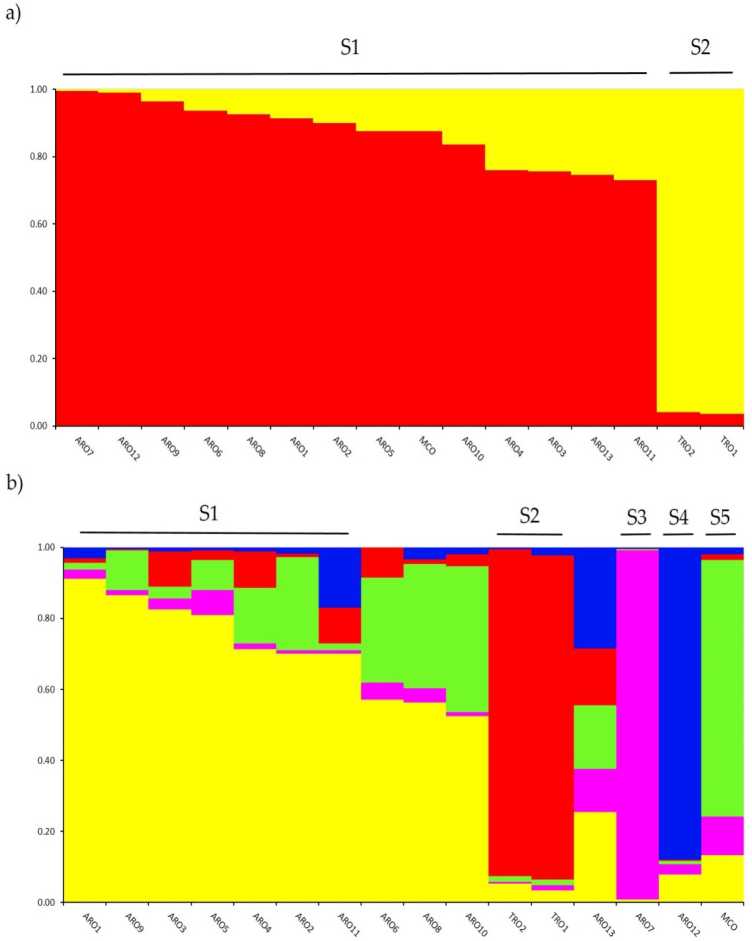
بررسی ساختار ژنتیکی در A. cepa مجموعه ژنوتیپ شده در این مطالعه با استفاده از تجزیه و تحلیل خوشهبندی مبتنی بر مدل ترکیبی پیادهسازی شده در نرمافزار STRUCTURE انجام شد. روش Evanno AK تقسیم بندی را در دو خوشه (K = 2) به عنوان آموزنده ترین برای ما پیشنهاد کرد. مجموعه داده,با پنجمe بعد بالاترین پak در K = 5 ( sopplementaiv Rgure S1). چنگال = 2، aاسب بخارopulations wپیش از این الاغigned همnوf دو خوشه با ضریب rnernbertoip (q) > 0.7. همانطور که shown در شکل 2a، اولین خوشه (به نام S1) شامل MCO و تمام جمعیت های ARO بود، در حالی که خوشه S2 دو جمعیت TRO را گروه بندی کرد. در K = 5، ارائه یک توصیف عمیق تر از مجموعه داده (شکل 2b75 درصد از الحاقات به یکی از پنج خوشه اختصاص داده شد. جدایی بین ARO (S1) و TRO (S2) تأیید شد، اگرچه برخی از جمعیتهای ARO مخلوط شدند (q <0.7) یا به طور جداگانه در دو خوشه جدید S3 و S4 (به ترتیب ARO7 و ARO12) گروهبندی شدند. جالب توجه است که نوع تجاری MCO یک خوشه متمایز (S5) را تشکیل می دهد که از پیاز قرمز آپولیا جدا شده است.
روابط ژنتیکی بین جمعیت ها
پلی مورفیسم SSR اجازه ترسیم دندروگرام از تنوع ژنتیکی را می دهد و نتایج آنالیز فیلوژنتیک در شکل نشان داده شده است. 3a. در اینجا، مجموعه ژرم پلاسم به پنج گروه تقسیم شد که به شدت توسط مقادیر بوت استرپ پشتیبانی میشوند. جمعیت های ARO7 و ARO12 بلافاصله از جمعیت های باقی مانده جدا شدند و دو خوشه مجزا را تشکیل دادند. خوشه سوم شامل دو جمعیت تجاری TRO بود، در همین حال گره چهارم MCO را از یازده جمعیت ARO تقسیم کرد. رابطه ژنتیکی که در بین جمعیت ها رخ می دهد با استفاده از تجزیه و تحلیل مختصات اصلی (PCoA) بیشتر مورد بررسی قرار گرفت (شکل 3b). همانطور که قبلاً مشخص شد، جمعیتهای ARO بهجز ARO12 و ARO7 که در موقعیتهای جدا شده در نمودار PcoA ظاهر شدند، بهطور محکم گروهبندی شدند. دو TRO و جمعیت MCO در پانل سمت راست پایین طرح پراکنده شدند.
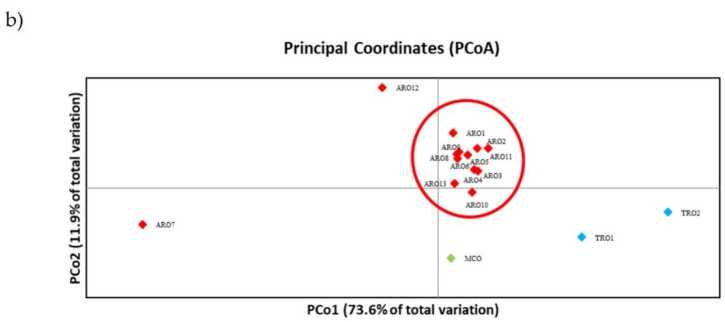
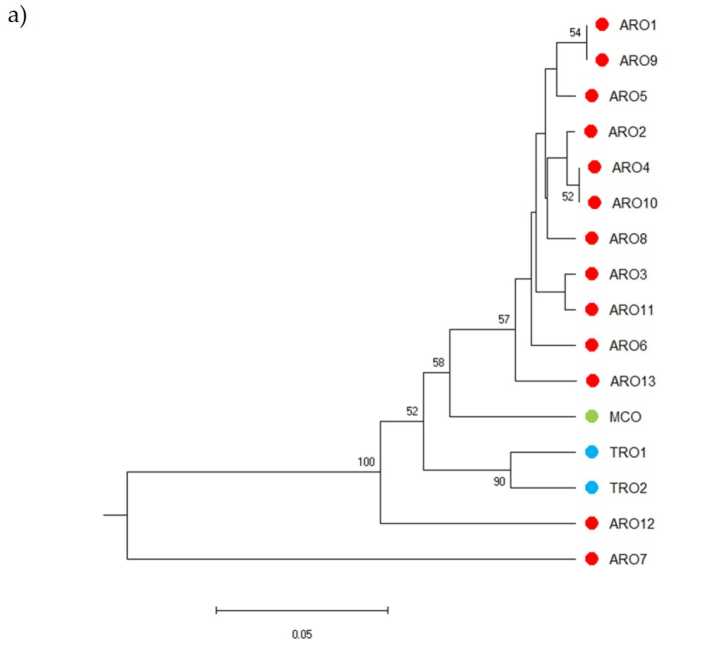
شکل 3. تنوع ژنتیکی در بین 16 A. cepa جمعیت مشخص شده در این مطالعه، بر اساس مشخصات SSR آنها. (a) دندروگرام UPGMA فاصله ژنتیکی. مقادیر پشتیبانی بوت استرپ > 50 در بالای گره های مربوطه نشان داده شده است. (bتجزیه و تحلیل اجزای اصلی (PCoA). این خوشه به رنگ قرمز دایره شده کاملاً با گروه تولید شده توسط تجزیه و تحلیل فیلوژنتیک و تشکیل شده توسط 11 الحاق ARO مطابقت دارد.
بحث
در میان مقدار زیادی از تنوع زیستی کشاورزی که به طور سنتی در جنوب ایتالیا کشت میشود، نژادهای بومی پیاز نشاندهنده محصولاتی هستند که باید از خطر فرسایش ژنتیکی و تهدید جایگزینی با ارقام مدرن محافظت شوند. در چارچوب پروژه منطقهای BiodiverSO، با هدف جمعآوری، توصیف، ترویج و حفاظت از منابع ژنتیکی منطقه آپولیا که به شدت با میراث محلی مرتبط است، مجموعهای از بذر از 13 جمعیت از نژاد بومی ARO را ایجاد کردیم. ما اولین ارزیابی تغییرات ARO را از نظر پلیمورفیسمهای DNA و دو پارامتر بیوشیمیایی، محتوای جامد محلول و اسید پیروویک، مرتبط با ویژگیهای طعم و اهمیت برای پذیرش محصولات تازه نپخته گزارش کردیم. علاوه بر این، دادههای مربوط به نژاد بومی ARO با دادههای جمعآوریشده در دو نژاد دیگر پیاز رنگدانهدار که اغلب با آنها اشتباه میشود، مقایسه شد.
آنالیزهای بیوشیمیایی بر اساس دستورالعملهای صنعت پیاز شیرین، شیرینی 13 جمعیت ARO مربوط به محتوای جامد محلول بالا و تندی متوسط را برجسته کرد. [31]. لامپ های ARO شیرین تر از لامپ های TRO و MCO بومی بودند و تندی کمی بالاتر از خود نشان دادند. با این حال، شیرینی در پیاز به دلیل تعادل بین محتوای قند و تندی است، بنابراین این خصوصیات میتواند برای حمایت از انتخاب ژنوتیپهای با ارزش، که معمولاً توسط کشاورزان فقط بر اساس مورفولوژی انجام میشود، مفید باشد.
نشانگرهای SSR به عنوان یک ابزار مفید برای تمایز ژنوتیپها تایید شد، البته در یک منطقه رشد باریک مانند شهر Acquaviva delle Fonti جمعآوری شدهاند. نشانگرهای انتخاب شده تعداد آلل های بیشتری را نسبت به نشانگرهایی که قبلاً توسط آنها گزارش شده بود، نمایش می دادند [43] و [44]، اما کمتر از نشانگرهای گزارش شده توسط [45]. علاوه بر این، 50٪ از مجموعه نشانگرهای ما مقادیر شاخص PIC را بیشتر از 0.5 نشان دادند، که ثابت می کند برای تمایز بین جمعیت ها در مجموعه مناسب است، همانطور که توسط پیشنهاد شده است. [46]. ارزیابی تنوع در جمعیت ها مقادیر مشابهی را بین Ho و He نشان داد که منجر به Fi پایین شدs ارزش های. این در توافق با ماهیت عبوری است A. cepa، که به طور جدی از افسردگی همخونی رنج می برد [47]. فی کلیs مقدار محاسبه شده در جمعیت های پیاز در نظر گرفته شده در این مطالعه (0.054) کمتر از مقداری بود که قبلا توسط [45] (0.22) و تقریباً مشابه آنچه توسط [31] (0.08) و [48] (0.00) که تنوع ژنتیکی را در نژادهای بومی پیاز از شمال غرب اسپانیا و نیجر ارزیابی کردند. سطوح قابل توجه هتروزیگوسیتی در جمعیت های ARO این تصور را تقویت می کند که آپولیا یک مرکز تنوع برای بسیاری از گونه های باغبانی است. [32، 42، 49-یک].
AMOVA تاکید کرد که بیشترین تنوع مولکولی در مجموعه ژنوتیپ شده در این مطالعه در جمعیت ها نهفته است. با این حال، تمایز ژنتیکی قابل توجهی در بین جمعیت ها (FPT مقادیر) وقوع لایه بندی ژنتیکی را نشان داد. در واقع، اگرچه نتایج ما حضور یکنواختی ژنتیکی را در اکثر جمعیتهای ARO نشان میدهد، که یک خوشه کاملاً تعریف شده را تشکیل میدهد، جمعیتهای ARO7 و ARO12 یک پروفایل ژنتیکی کاملاً متمایز را نشان میدهند. این نتیجه می تواند به دلیل منشا متفاوت بذرهای مورد استفاده دو کشاورز که جمعیت ها از آنها جمع آوری شده اند باشد. علاوه بر این، بر اساس نتایج بهدستآمده، توده ARO را میتوان به وضوح در سطح ژنتیکی از تودههای TRO و MCO متمایز دانست. در یک مطالعه اخیر، [29] تنوع ژنتیکی چندین نژاد پیاز ایتالیایی از جمله "Acquaviva"، "Tropea" و "Montoro" را ارزیابی کرد. اگرچه نویسندگان از نشانگرهای SNP برای ارزیابی تنوع ژنتیکی مجموعه وسیعتری از پیاز استفاده کردند، ژنوتیپسازی قادر به تشخیص «Acquaviva» از «Tropea» و «Montoro» نبود. احتمالاً، این اختلاف به دلیل میانگین پایین مقدار PIC یافت شده (0.292) است که نشان دهنده اطلاعات عمومی مختصری از مکان های تحت تجزیه و تحلیل است که توسط ادعا شده است. [29]. علاوه بر این، به منظور بررسی وجود زیرساختار در خوشه ایتالیایی آنها، بهتر بود ژنوتیپ های ایتالیایی جدا از بقیه مجموعه مورد تجزیه و تحلیل قرار می گرفت. احتمالاً به تجسم الگوی تنوع ژنتیکی مرتبط با طبقه بندی جغرافیایی یا صفات تحت انتخاب تجربی اجازه می داد.
در نتیجه، مطالعه حاضر گزارشی جامع در مورد یک نژاد پیاز مرتبط با میراث فرهنگی محلی و دارای اهمیت اقتصادی برای کشاورزان است. نتایج ما نشان میدهد که، به استثنای چند مورد، ARO با یک مخزن ژنی کاملاً تعریف شده مشخص میشود، که شایسته است از خطر فرسایش ژنتیکی محافظت شود. از این رو، ایجاد مجموعه ای نماینده از این منبع ارزشمند تنوع ژنتیکی بسیار مهم بوده است. در نهایت، خصوصیات ژنتیکی و فنوتیپی ARO ممکن است برای به دست آوردن علائم کیفیت از اتحادیه اروپا مفید باشد.
مواد و روش ها
جمع آوری ژرم پلاسم، مواد گیاهی و استخراج DNA
مجموعه ای از 13 جمعیت از نژاد بومی ARO در چارچوب یک پروژه منطقه آپولیا (BiodiverSO: https://www.biodiversitapuglia.it/)، از طریق مجموعه ای از ماموریت های انجام شده در "Acquaviva delle Fonti"، یک شهر کوچک آپولیایی در استان باری، ایتالیا. مکانهای گردآوری هر عضو از طریق سیستم اطلاعات جغرافیایی (GIS) نقشهبرداری و در جدول گزارش شده است 4. علاوه بر این، دو جمعیت از نژاد بومی TRO و یک جمعیت از نژاد بومی MCO در مطالعه حاضر وارد شدند و به عنوان مرجع مورد استفاده قرار گرفتند. تمام مواد گیاهی در شرایط محیطی یکسان در مزرعه آزمایشی "P Martucci" از دانشگاه باری (41° 1'22.08" شمالی، 16°54'25.95" E) در زیر قفس حفاظتی برای جلوگیری از گرده افشانی متقاطع کشت شدند. جمعيت ها و اطمينان از گرده افشاني درون جمعيتي با استفاده از مگس ها (لوسیلیا سزار). 16 جمعیت برای صفات مربوط به اندازه و شکل پیاز و رنگ پوست و گوشت مشخص شدند (جدول S1). علاوه بر این، سنجش محتوای محلول جامد با استفاده از رفرکتومتر دستی انجام شد و تندی در نمونههای آب پیاز با افزودن 2,4،0.125-دینیتروفنیل هیدرازین (XNUMX/XNUMX درصد) اندازهگیری شد. v/v در 2N HCl) و ارزیابی جذب در 420 نانومتر، همانطور که توسط گزارش شده است [31]. آزمون چند برد دانکن و آزمون SNK برای تعیین وجود تفاوت معنیدار انجام شد.
جدول 4. فهرست جمعیت های جمع آوری شده و ژنوتیپ شده در این مطالعه. برای هر جمعیت، کد شناسایی، نام محلی، مختصات GPS و بانک ژن حفظ بذر گزارش شده است.
| رمز | نام | مختصات GPS | بانک ژن y |
| ARO1 | سیپولا روسا دی آکواویوا | 40°54’21.708″ N 16°49’1.631” E | Di.SSPA |
| ARO2 | سیپولا روسا دی آکواویوا | 40°53’14.28″ N 16°48’56.879” E | Di.SSPA |
| ARO3 | سیپولا روسا دی آکواویوا | 40°54’11.304″ N 16°49’13.079” E | Di.SSPA |
| ARO4 | سیپولا روسا دی آکواویوا | 40°54’3.348″ N 16°40’27.011” E | Di.SSPA |
| ARO5 | سیپولا روسا دی آکواویوا | 40°51’59.76″ N 16°53’0.527” E | Di.SSPA |
| ARO6 | سیپولا روسا دی آکواویوا | 40°52’48.72″ N 16°49’43.247” E | Di.SSPA |
| ARO7 | سیپولا روسا دی آکواویوا | 40°53’13.47″ N 16°50’23.783” E | Di.SSPA |
| ARO8 | سیپولا روسا دی آکواویوا | 40°53’18.816″ N 16°49’33.888” E | Di.SSPA |
| ARO9 | سیپولا روسا دی آکواویوا | 40°54'51.372 اینچ N 16°49'3.504" E | Di.SSPA |
| ARO10 | سیپولا روسا دی آکواویوا | 40°54’1.188″ N 16°49’24.311” E | Di.SSPA |
| ARO11 | سیپولا روسا دی آکواویوا | 40°52'49.8 اینچ N 16°49'48.575" E | Di.SSPA |
| ARO12 | سیپولا روسا دی آکواویوا | 40°52’38.892″ N 16°49’28.379” E | Di.SSPA |
| ARO13 | سیپولا روسا دی آکواویوا | 40°53’21.768″ N 16°49’29.711” E | Di.SSPA |
| TRO1 | Cipolla rossa lunga di Tropea | - | Di.SSPA |
| TRO2 | Cipolla rossa tonda di Tropea | - | Di.SSPA |
| MCO | سیپولا راماتا دی مونتورو | - | Di.SSPA |
| y Di.SSPA، گروه علوم خاک، گیاهان و مواد غذایی، دانشگاه باری. |
مواد برگ از 20 ژنوتیپ در هر جمعیت نمونه برداری شد و تا زمان استفاده در دمای 80- درجه سانتی گراد نگهداری شد. برای گونه های غنی از پلی ساکارید، به عنوان A. cepa، اولین مراحل حذف پلی ساکارید برای به دست آوردن DNA با کیفیت خوب ضروری است، بنابراین شستشوهای اولیه در بافر STE (0.25 مولار ساکارز، 0.03 M Tris، 0.05 M EDTA) همانطور که توسط [52]. DNA کل به روش CTAB استخراج شد [53] و در نهایت کیفیت و غلظت آن توسط اسپکتروفتومتر UV-vis Nano Drop 2000 (ThermoScientific, Waltham, MA, USA) و الکتروفورز ژل آگارز 0.8% بررسی شد.
تجزیه و تحلیل SSR
16 ترکیب آغازگر EST-SSR که توسط [54] و قبلا در مطالعات تنوع ژنتیکی توسط [43] و [44] و 21 SSR ژنومی [45-یک] برای ارزیابی مناسب بودن آنها غربالگری شدند (جدول تکمیلی S4). ژنوتیپ با استفاده از روش برچسب گذاری فلورسنت اقتصادی انجام شد که در آن دم M13 به هر آغازگر SSR رو به جلو اضافه می شود. [56]. مخلوط های PCR در 20 گرم لیتر واکنش حاوی: 50 نانوگرم DNA کل، 0.2 میلی مولار مخلوط dNTP، 1X بافر واکنش PCR، 0.8 واحد DNA پلیمراز DreamTaq (Thermo Scientific، Waltham، MA، USA)، 0.16 گرم مولار پرایمر معکوس تهیه شد. ، 0.032 گرم پرایمر جلو با توالی M13 (5'-TGTAAAACGACGGCCAGT-3') و 0.08 گرم پرایمر جهانی M13 با رنگ های فلورسنت FAM یا NED (Sigma-Aldrich, St. Louis, MO, USA) گسترش یافته است. واکنشهای PCR در ترموسایکلر SimpliAmp (Applied Biosystems، CA، USA) با شرایط زیر برای اکثر جفتهای پرایمر انجام شد: 94 درجه سانتیگراد برای 5 دقیقه، 40 چرخه در دمای 94 درجه سانتیگراد برای 30 ثانیه، 58 درجه سانتیگراد. برای 45 ثانیه و 72 درجه سانتیگراد به مدت 45 ثانیه و افزایش طول نهایی در 72 درجه سانتیگراد به مدت 5 دقیقه. همانطور که برای ACM446 و ACM449، یک تاچ داون PCR با بازپخت 60 درجه سانتیگراد تا 55 درجه سانتیگراد در 10 سیکل، 30 سیکل در دمای 55 درجه سانتیگراد، و به دنبال آن تمدید نهایی 5 دقیقه در دمای 72 درجه سانتیگراد اعمال شد. محصولات PCR در یک صفحه 96 چاهی بارگذاری شده و با 14 گرم لیتر Hi-Di Formamide (Life Technologies, Carlsbad, CA, USA) و 0.5 gL GeneScan 500 ROX Size Standard (Life Technologies, Carlsbad, CA, USA) مخلوط شدند. آمپلیکون ها با استفاده از دستگاه توالی یابی مویرگی ABI PRISM 3100 Avant Genetic Analyzer (Life Technologies، Carlsbad، CA، USA)، که در آن آلل ها به عنوان هم غالب رتبه بندی شدند و با استفاده از نرم افزار GeneMapper نسخه 3.7 تخصیص داده شدند.
نرم افزار GenAlEx 6.5 [57] و Cervus 3.0.7 [58] برای تخمین تعداد آلل ها (Na)، تعداد آلل های موثر (Ne)، هتروزیگوسیتی مشاهده شده (Ho)، هتروزیگوسیتی مورد انتظار (He)، محتوای اطلاعات چندشکلی (PIC)، شاخص اطلاعات شانون (I) و شاخص تثبیت (Fis) استفاده شد. ) برای هر مکان SSR.
ارزیابی تنوع ژنتیکی
تقسیم بندی سلسله مراتبی تنوع ژنتیکی بین و درون جمعیت های پیاز توسط GenAlEx 6.5 ارزیابی شد. [57] از طریق تجزیه و تحلیل واریانس مولکولی (AMOVA) با 999 bootstrapping برای آزمایش اهمیت. علاوه بر این، از نرم افزار GenAlEx 6.5 برای تخمین تنوع در هر جمعیت با محاسبه میانگین Ho، He و Fis در تمام جایگاه های SSR استفاده شد.
ساختار جمعیت توسط الگوریتم خوشهبندی مبتنی بر مدل بیزی که در نرمافزار STRUCTURE v.2.3.4 پیادهسازی شده است، استنباط شد. [59]. مجموعه داده ها با تعدادی خوشه فرضی (K)، از 1 تا 10 اجرا شد، که ده اجرا مستقل را برای هر مقدار K تنظیم می کند. برای هر اجرا، با هدف تأیید سازگاری نتایج، 100,000 دوره سوختگی اولیه و 100,000 تکرار زنجیره مارکوف مونت کارلو (MCMC) تحت مدل ترکیبی و فرکانسهای آللی مستقل در بین جمعیتها انجام شد. محتملترین مقدار K با اجرای روش AK تعیین شد که توسط [60]، در برنامه مبتنی بر وب SRUCTURE HARVESTER [61]. یک جمعیت زمانی به یک خوشه خاص اختصاص داده شد که ضریب عضویت آن (Q-value) بالاتر از 0.7 بود، در غیر این صورت از تبار مختلط در نظر گرفته شد.
تجزیه و تحلیل مختصات اصلی به منظور تجسم الگوهای رابطه ژنتیکی بین الحاقات نشان داده شده توسط ماتریس فاصله ژنتیکی Nei انجام شد (جدول تکمیلی S5). بر اساس بسامدهای آللی، دندروگرام فاصله ژنتیکی با اجرای روش گروه زوج وزن نشده با تحلیل خوشهای میانگینهای حسابی (UPGMA) در نرمافزار POPTREEW ساخته شد. [62]. بوت استرپینگ برای ارزیابی اطمینان در خوشهبندی سلسله مراتبی استفاده شد و 100 نمونهگیری مجدد از مجموعه داده را تنظیم کرد. در نهایت نرم افزار MEGA X [63] به عنوان نرم افزار ترسیم درخت استفاده شد.
مواد تکمیلی: زیر در دسترس هستند آنلاین در http://www.mdpi.com/2223-7747/9/2/260/s1. جدول S1: مشخصات مورفولوژیکی لامپ های ARO، MCO و TRO. جدول S2: شاخص های هتروزیگوسیتی و تثبیت برای توده های بومی ARO و توده های TRO و MCO محاسبه شده است. جدول S3: مقادیر زوجی پارامتر Fpt. جدول S4: فهرست SSR های مورد استفاده در مطالعه. جدول S5. ماتریس جمعیت دوتایی فاصله ژنتیکی نی. شکل S1: نمودار خطی مقادیر K در حال تغییر با دلتا K ایواننو.
مقالات نویسنده: CL و LR مطالعه را تصور کردند و آزمایش را طراحی کردند. CL و PI آنالیز نشانگر مولکولی را انجام دادند. ARM و VZ آزمایشات میدانی را انجام دادند. RM، SP، GR، و CL در تجزیه و تحلیل داده ها درگیر شدند. RM و CL دست نوشته را نوشتند. همه نویسندگان نسخه منتشر شده نسخه خطی را خوانده و با آن موافقت کرده اند.
بودجه: این کار توسط پروژه منطقهای آپولیایی "تنوع زیستی گونههای سبزیجات آپولیایی" - Programma di Sviluppo Rurale per la Puglia 2014-2020 تامین شده است. Misura 10-Sottomisura 10.2; کمک مالی CUP H92C15000270002، ایتالیا.
تقدیرنامه ها: قدردانی از "Azienda Agricola Iannone Anna" و "Associazione produttori della vera cipolla rossa di Acquaviva" برای تهیه مواد گیاهی مورد استفاده در آزمایش است.
تضاد منافع: نویسندگان هیچ گونه تضاد منافع را اعلام نمی کنند.
منابع
- 1. Stearn، WT چند گونه از آلیوم شناخته شده است؟ کیو مگ. 1992, 9، 180-182. [CrossRef]
- 2. FAOSTAT. پایگاه آماری فائو در دسترس آنلاین: http://www.fao.org/2017 (در 8 ژانویه 2019 قابل دسترسی است).
- 3. بلوک، E. شیمی سیر و پیاز. علم صبح. 1985, 252، 114-119. [CrossRef]
- 4. لی، بی. یونگ، جی اچ. ارزیابی کیم، HS پیاز قرمز بر فعالیت آنتی اکسیدانی در موش صحرایی. مواد شیمیایی مواد غذایی سموم 2012, 50، 3912-3919. [CrossRef]
- 5. لی، اس ام. ماه، جی. چانگ، جی اچ. چا، YJ; Shin, MJ اثر عصاره پوست پیاز غنی از کورستین بر ترومبوز شریانی در موش صحرایی. مواد شیمیایی مواد غذایی سموم 2013, 57، 99-105. [CrossRef] [PubMed]
- 6. یوشیناری، او. شیوجیما، ی. ایگاراشی، ک. اثرات ضد چاقی عصاره پیاز در موش های چرب دیابتی زوکر. مواد مغذی 2012, 4,1518 1526. [CrossRef]
- 7. آکاش، MSH; رحمان، ک. Chen, S. Spice plant Allium cepa: مکمل غذایی برای درمان دیابت نوع 2. تغذیه 2014, 30، 1128-1137. [CrossRef] [PubMed]
- 8. وانگ، ی. تیان، WX; Ma, XF اثرات بازدارنده پیاز (Allium cepa L.) عصاره بر تکثیر سلولهای سرطانی و سلولهای چربی از طریق مهار اسید چرب سنتاز. پیمان آسیایی J. Cancer Prev. 2012,13، 5573-5579. [CrossRef] [PubMed]
- 9. لای، WW; Hsu، SC; چوه، FS; چن، YY; یانگ، جی اس. لین، جی پی؛ Lien, JC; تسای، CH; Chung، JG Quercetin از طریق مهار مسیرهای سیگنالینگ NF-kappaB و ماتریکس متالوپروتئیناز-2/-9، مهاجرت و تهاجم به سلول های سرطانی دهان انسان SAS را مهار می کند. ضد سرطان Res. 2013, 33، 1941-1950. [PubMed]
- 10. نیکاسترو، HL; راس، SA; Milner، JA سیر و پیاز: خواص پیشگیری از سرطان آنها. سرطان قبلی Res. 2015, 8,181 189. [CrossRef]
- 11. فورته، ال. توریچلی، پی. بوانینی، ای. گازانو، م. روبینی، ک. فینی، م. Bigi, A. خواص آنتی اکسیدانی و ترمیم استخوان هیدروکسی آپاتیت عاملدار شده با کوئرستین: مطالعه کشت مشترک سلولهای استئوبلاست-استئوکلاست-اندوتلیال در شرایط آزمایشگاهی. Acta Biomater. 2016, 32، 298-308. [CrossRef]
- 12. یامازاکی، ی. ایوازاکی، ک. میکامی، م. Yagihashi، A. توزیع یازده پیش ساز طعم، مشتقات S-Alk(en)yl-L-cysteine، در هفت سبزی آلیوم. علوم غذایی تکنولوژی Res. 2011, 17، 55-62. [CrossRef]
- 13. Block, E. شیمی آلی گوگرد از جنس Allium - مفاهیم برای شیمی آلی گوگرد. آنژو. شیمی. بین المللی اد. انگلیسی 1992, 31، 1135-1178. [CrossRef]
- 14. گریفیث، جی. ترومن، ال. کروتر، تی. توماس، بی. اسمیت، بی پیاز - یک فایده جهانی برای سلامتی. فیتوتر. Res. 2002,16، 603-615. [CrossRef]
- 15. شویمر، اس. Weston, WJ توسعه آنزیمی اسید پیروویک در پیاز به عنوان معیار تندی. جی. آگریک. مواد شیمیایی مواد غذایی 1961, 9، 301-304. [CrossRef]
- 16. کتر، گربه; Randle، WM ارزیابی تندی در پیاز. که در مطالعات آزمایش شده برای آموزش آزمایشگاهی. کارچر، اس جی، اد. انجمن آموزش آزمایشگاهی زیست شناسی (ABLE): نیویورک، نیویورک، ایالات متحده آمریکا، 1998; جلد 19، ص 177-196.
- 17. هانلت، P تاکسونومی، تکامل و تاریخ. که در پیاز و محصولات متفقین، جلد. I. گیاه شناسی، فیزیولوژی و ژنتیک. Rabinowitch، HD، Brewster، JL، Eds. CRC Press: Boca Raton، FL، USA، 1990; ص 1-26.
- 18. رابینوویچ، HD; کورا، ال. Allium Crop Science: پیشرفت های اخیر. انتشارات CABI: Wallingford، انگلستان، 2002.
- 19. مالور، سی. کاراودو، ام. استوپانان، جی. Mallor, F. خصوصیات منابع ژنتیکی پیاز (Allium cepa L.) از مرکز ثانویه تنوع اسپانیایی. طول. جی. آگریک. Res. 2011, 9، 144-155. [CrossRef]
- 20. فریولی، ف. D'Antuono، LF ارزیابی فنول ها و سولفوکسیدهای سیستئین در ژرم پلاسم محلی پیاز و موسیر از ایتالیا و اوکراین. ژنت منبع. Crop Evol. 2016, 63، 601-614. [CrossRef]
- 21. پتروپولوس، SA; فرناندز، آ. باروس، ال. فریرا، ICFR؛ Ntatsi، G. توصیف مورفولوژیکی، تغذیه ای و شیمیایی 'vatikiotiko'، یک نژاد محلی پیاز از یونان. شیمی مواد غذایی. 2015,182، 156-163. [CrossRef]
- 22. لیگوری، ال. آدیلتا، جی. نازارو، اف. فراتیانی، اف. دی متئو، ام. آلبانیز، دی. خواص بیوشیمیایی، آنتی اکسیدانی و فعالیت ضد میکروبی ارقام مختلف پیاز در منطقه مدیترانه. جی. مواد غذایی. شخصیت. 2019,13، 1232-1241. [CrossRef]
- 23. یو، KS; پایک، ال. کرازبی، ک. جونز، آر. Leskovar, D. تفاوت در تندی پیاز به دلیل ارقام، محیط رشد و اندازه پیاز. علمی هورتیک. 2006,110، 144-149. [CrossRef]
- 24. بیسک، ن. پرنر، اچ. شوارتز، دی. جورج، ای. Kroh، LW; Rohn, S. توزیع کوئرستین-3، 4'-O-دیگلوکوزید، کوئرستین-4'-O-مونوگلوکوزید، و کورستین در قسمت های مختلف پیاز پیاز (Allium cepa L.) تحت تاثیر ژنوتیپ. شیمی مواد غذایی. 2010,122، 566-571. [CrossRef]
- 25. کاروسو، جی. کونتی، اس. ویلاری، گ. بورلی، سی. ملکیونا، جی. مینوتولو، ام. روسو، جی. اثرات زمان کاشت و تراکم بوته بر عملکرد، کیفیت و محتوای آنتی اکسیدانی پیاز (Allium cepa L.) در جنوب ایتالیا. علمی هورتیک. 2014,166، 111-120. [CrossRef]
- 26. پرز-گرگوریو، MR; رگیرو، جی. سیمال گاندارا، ج. رودریگز، اس. Almeida، DPF افزایش ارزش افزوده پیاز به عنوان منبع فلاونوئیدهای آنتی اکسیدانی: یک بررسی انتقادی. ترس مجله علوم غذایی. نتر 2014, شماره ۱۰۲۹،1050 1062. [CrossRef] [PubMed]
- 27. پونل، تی. شوایگرت، آر.ام. تاثیر روش کشت و انتخاب رقم بر کربوهیدرات های محلول و اصول تند در پیاز (Allium cepa L.). جی. آگریک. مواد شیمیایی مواد غذایی 2018, 66، 12827-12835. [CrossRef] [PubMed]
- 28. تدسکو، آی. کربن، V. Spagnuolo، C. میناسی، پ. Russo، GL شناسایی و تعیین کمیت فلاونوئیدها از دو رقم ایتالیای جنوبی آلیوم سیپا L.، Tropea (پیاز قرمز) و Montoro (پیاز مس)، و ظرفیت آنها برای محافظت از گلبول های قرمز انسان در برابر استرس اکسیداتیو. جی. آگریک. مواد شیمیایی مواد غذایی 2015, 63، 5229-5238. [CrossRef]
- 29. ویلانو، سی. اسپوزیتو، اس. کاروچی، اف. فروسیانته، ال. کارپوتو، دی. Aversano، R. ژنوتیپ با توان عملیاتی بالا در پیاز ساختار تنوع ژنتیکی و SNP های آموزنده مفید برای اصلاح مولکولی را نشان می دهد. مول. نژاد. 2019, 39، 5. [CrossRef]
- 30. مرکاتی، ف. لونگو، سی. پوما، دی. آرانیتی، ف. لوپینی، ا. مامانو، م.م. فیوره، ام سی؛ آبناولی، MR; Sunseri، F تنوع ژنتیکی یک گوجه فرنگی ایتالیایی با ماندگاری طولانی ( Solanum lycopersicum L.) جمع آوری با استفاده از SSR و صفات مورفولوژیکی میوه. ژنت منبع. Crop Evol. 2014, 62، 721-732. [CrossRef]
- 31. گونزالس پرز، س. مالور، سی. Garces-Claver، A.; مرینو، اف. تابودا، ا. ریورا، ا. پومار، اف. پروویچ، دی. Silvar, C. بررسی تنوع ژنتیکی و صفات کیفی در مجموعه ای از پیاز (Allium cepa L.) نژادهای بومی از شمال غربی اسپانیا. ژنتیک 2015, 47، 885-900. [CrossRef]
- 32. لوتی، سی. آیووینو، پی. سنتومنی، آی. Marcotrigiano، AR; فانلی، وی. میمیولا، جی. سامو، سی. پاوان، س. Ricciardi، L. خصوصیات ژنتیکی، زیستی زراعی و تغذیه ای کلم پیچ (Brassica oleracea L. var. آسفالا) تنوع در آپولیا، جنوب ایتالیا. تنوع 2018,10، 25. [CrossRef]
- 33. باردارو، ن. مارکوتریجیانو، آر. براکوتو، وی. مازئو، آر. ریکاردی، اف. لوتی، سی. پاوان، س. Ricciardi، L. تجزیه و تحلیل ژنتیکی مقاومت به اوروبانچ کرناتا (فورسک.) در نخود (Pisum sativum L) خط کم استریگولاکتون. جی. پاتول گیاهی. 2016, شماره ۱۰۲۹، 671 675.
- 34. واکو، ت. تسوکازاکی، اچ. یاگوچی، س. یاماشیتا، ک. ایتو، اس. شیگیو، ام. نقشه برداری از جایگاه های کمی برای زمان پیچ شدن در پیاز خوشه ای (آلیوم فیستولوزوم L.). یوفیتیکا 2016, 209، 537-546. [CrossRef]
- 35. داکا، ن. موخوپادهایای، ع. پریتوش، ک. گوپتا، وی. پنتال، دی. پرادان، AK شناسایی SSRهای ژنتیک و ساخت یک نقشه پیوند مبتنی بر SSR در براسیکا جونسیا. یوفیتیکا 2017, 213، 15 [CrossRef]
- 36. آناندان، س. Mote، SR; گوپال، جی. ارزیابی هویت واریته پیاز با استفاده از نشانگرهای SSR. Seed Sci. تکنولوژی 2014, 42، 279-285. [CrossRef]
- 37. میتروا، ک. سوبودا، پ. Ovesna, J. انتخاب و اعتبار یک مجموعه نشانگر برای تمایز ارقام پیاز از جمهوری چک. چک جی ژنت. نژاد گیاهی. 2015, 51، 62-67. [CrossRef]
- 38. دی رینزو، وی. Miazzi، MM; فانلی، وی. سابتا، دبلیو. Montemurro، C. حفظ و توصیف تنوع زیستی ژرم پلاسم زیتون آپولین. Acta Hortic. 2018,شماره ۱۰۲۹،1 6. [CrossRef]
- 39. مالور، سی. آرندو آندرس، ا. Garces-Claver، A. ارزیابی تنوع ژنتیکی اسپانیایی آلیوم سیپا نژادهای بومی برای پرورش پیاز با استفاده از نشانگرهای ریزماهواره. علمی هورتیک. 2014,170، 24-31. [CrossRef]
- 40. ریورا، ا. مالور، سی. Garces-Claver، A.; گارسیا اولوآ، آ. پومار، اف. سیلوار، سی. ارزیابی تنوع ژنتیکی در پیاز (آلیوم سیپا L.) نژادهای بومی شمال غربی اسپانیا و مقایسه با تنوع اروپایی. NZJ Crop Hortic. 2016, 44، 103-120. [CrossRef]
- 41. دی جیووانی، سی. پاوان، س. تارانتو، اف. دی رینزو، وی. Miazzi، MM; Marcotrigiano، AR; مانگینی، جی. مونتمورو، سی. ریکاردی، ال. لوتی، سی. تنوع ژنتیکی مجموعه ژرم پلاسم جهانی نخود (Cicer arietinum L.) از جمله الحاقات ایتالیایی در معرض خطر فرسایش ژنتیکی. فیزیول. مول. Biol. گیاهان 2017, 23، 197-205. [CrossRef]
- 42. مازئو، آر. Morgese، A.; سونانت، جی. Zuluaga، DL; پاوان، س. ریکاردی، ال. لوتی، سی. تنوع ژنتیکی در کلم بروکلی (براسیکا راپا L. subsp. سیلوستریس (L.) Janch.) از جنوب ایتالیا. علمی هورتیک. 2019, 253، 140-146. [CrossRef]
- 43. جاکس، م. مارتین، دبلیو. مک کالوم، جی. Havey، M. پلی مورفیسم های تک نوکلئوتیدی، ایندل ها و تکرارهای توالی ساده برای شناسایی رقم پیاز. مربا. Soc. هورتیک. علمی 2005,130، 912-917. [CrossRef]
- 44. مک کالوم، جی. تامسون، اس. پیتر-جویس، ام. Kenel, F. تجزیه و تحلیل تنوع ژنتیکی و توسعه نشانگر پلی مورفیسم تک نوکلئوتیدی در پیاز پیاز پرورشی بر اساس نشانگرهای تکراری توالی برچسب-ساده توالی بیان شده. مربا. Soc. هورتیک. علمی 2008,133، 810-818. [CrossRef]
- 45. بالدوین، اس. پیتر-جویس، ام. رایت، ک. چن، ال. مک کالوم، جی. توسعه نشانگرهای تکراری توالی ساده ژنومی قوی برای تخمین تنوع ژنتیکی درون و بین پیاز پیاز (Allium cepa L.) جمعیت. مول. نژاد. 2012, 30، 1401-1411. [CrossRef]
- 46. دی وودی، جی. Honeycutt, RL; نشانگرهای ریزماهواره Skow، LC در گوزن دم سفید. جی. هرد. 1995, شماره ۱۰۲۹، 317 319. [CrossRef] [PubMed]
- 47. خدادادی، م. حسن پناه، د. پیاز ایرانی (Allium cepa L.) پاسخ ارقام به افسردگی همخونی. برنامه جهانی علمی جی. 2010,11، 426-428.
- 48. عبدو، ر. باکاسو، ی. سعدو، م. Baudoin، JP; هاردی، OJ تنوع ژنتیکی پیاز نیجر (Allium cepa L.) توسط نشانگرهای تکرار توالی ساده (SSR) ارزیابی شد. Acta Hortic. 2016,شماره ۱۰۲۹، 77 90. [CrossRef]
- 49. پاوان، س. لوتی، سی. Marcotrigiano، AR; مازئو، آر. باردارو، ن. براکوتو، وی. ریکاردی، اف. تارانتو، اف. داگوستینو، ن. شیاوولی، ا. و همکاران یک خوشه ژنتیکی متمایز در نخود پرورشیافته که با کشف نشانگر و ژنوتیپ در سطح ژنوم آشکار شد. ژنوم گیاهی 2017, شماره ۱۰۲۹،10. [CrossRef]
- 50. پاوان، س. Marcotrigiano، AR; سیانی، ای. مازئو، آر. زونو، وی. روگیری، وی. لوتی، سی. Ricciardi، L. ژنوتیپ کردن با توالی یابی خربزه (Cucumis melo L.) جمع آوری ژرم پلاسم از یک مرکز ثانویه تنوع، الگوهای تنوع ژنتیکی و ویژگی های ژنومی استخرهای ژنی مختلف را برجسته می کند. BMC Genom. 2017, 18، 59. [CrossRef]
- 51. دی رینزو، وی. سیون، اس. تارانتو، اف. داگوستینو، ن. مونتمورو، سی. فانلی، وی. سابتا، دبلیو. بوشفا، اس. تمندجری، ع. پاسکوالون، آ. و همکاران جریان ژنتیکی در میان جمعیت زیتون در حوضه مدیترانه همتا جی. 2018, 6. [CrossRef]
- 52. شپرد، LD; McLay، TG دو پروتکل در مقیاس میکرو برای جداسازی DNA از بافت گیاهی غنی از پلی ساکارید. J. Plant Res. 2011,124، 311-314. [CrossRef]
- 53. دویل، جی جی; دویل، JL جداسازی DNA گیاه از بافت تازه. تمرکز 1990,12، 13-14.
- 54. Kuhl, JC; چونگ، اف. کیائوپینگ، ی. مارتین، دبلیو. زودی، ی. مک کالوم، جی. کاتاناخ، ا. رادرفورد، پی. سینک، KC; جندرک، م. و همکاران مجموعه ای منحصر به فرد از 11,008 برچسب توالی بیان شده پیاز، توالی بیان شده و تفاوت های ژنومی را بین ردیف های تک لپه ای مارچوبه و پوال نشان می دهد. سلول گیاه 2004,16، 114-125. [CrossRef]
- 55. کیم، اچ جی; لی، منابع انسانی؛ هیون، جی. آهنگ، خ. کیم، KH; کیم، جی. هور، سی جی؛ توسعه نشانگر هارن، CH برای آزمایش خلوص ژنتیکی پیاز با استفاده از SSR Finder. کره ای J. Breed. علمی 2012, 44، 421-432. [CrossRef]
- 56. Schuelke, M. یک روش اقتصادی برای برچسب زدن فلورسنت قطعات PCR. نات. بیوتکنول 2000, 18، 233-234. [CrossRef] [PubMed]
- 57. پیکال، ر. Smouse، PE GenAlEx 6.5: تجزیه و تحلیل ژنتیک در اکسل. نرم افزار ژنتیک جمعیت برای آموزش و پژوهش: به روز رسانی. بیوانفورماتیک 2012, 28، 2537-2539. [CrossRef] [PubMed]
- 58. Kalinowski، ST; Taper، ML; مارشال، TC بازنگری در برنامه کامپیوتری CERVUS که چگونه خطای ژنوتیپ را تطبیق می دهد، موفقیت در انتساب پدری را افزایش می دهد. مول. Ecol. 2007,16، 1099-1106. [CrossRef]
- 59. پریچارد، جی کی; استفنز، ام. روزنبرگ، NA; دانلی، P. نقشه برداری انجمن در جمعیت های ساختار یافته. صبح. جی. هوم. ژنت 2000, شماره ۱۰۲۹، 170 181. [CrossRef]
- 60. ایوانو، جی. رگنات، اس. Goudet, J. تشخیص تعداد خوشههای افراد با استفاده از نرمافزار SRUCTURE: یک مطالعه شبیهسازی. مول. Ecol. 2005,14، 2611-2620. [CrossRef]
- 61. ارل، دی. VonHoldt, B. STRUCTURE HARVESTER: وب سایت و برنامه ای برای تجسم خروجی ساختار و پیاده سازی روش Evanno. حفظ کنید. ژنت منبع. 2011, 4. [CrossRef]
- 62. تاکزاکی، ن. نی، م. Tamura, K. POPTREEW: نسخه وب POPTREE برای ساخت درختان جمعیت از داده های فرکانس آللی و محاسبه برخی کمیت های دیگر. مول. Biol. تکامل. 2014, شماره ۱۰۲۹، 1622 1624. [CrossRef]
- 63. کومار، س. استچر، جی. لی، ام. کنیاز، سی. Tamura، K. MEGA X. تجزیه و تحلیل ژنتیک تکاملی مولکولی در پلتفرمهای محاسباتی. مول. Biol. تکامل. 2018, 35، 1547-1549. [CrossRef]